限制酶种类知多少(下)
在限制酶种类知多少(上)中,我们介绍了细菌的“限制-修饰”(R-M) 系统,限制酶的命名方式,Type I限制酶和Type II中几个主要的亚类。这期我们来继续了解其他的限制酶种类。
04 Type II(接上期)
▶Type IIA
Type IIA类限制酶识别非对称 (asymmetric) 序列,并在识别序列内部或距离识别序列特定距离的位点切割。因此,很多识别非回文序列的Type IIS亚类限制酶,如BspQI (GCTCTTC(1/4)),同时也属于Type IIA亚类。
▶Type IIE
Type IIE是一类特殊的Type IIP亚类,单体蛋白在催化结构域之外,还包含一个变构效应结构域 (allosteric effector domains),两个单体再组成同源二聚体。与普通的Type IIP限制酶不同,Type IIE类限制酶需要同一条DNA底物上有两个识别位点才能更有效行使功能,其中一个识别位点与催化结构域结合作为切割位点,另一个与变构结构域结合,作为激活位点增强酶的活性。这一类型的典型代表是EcoRII/PspGI (/CCWGG) 和NaeI (GCC/GGC)。
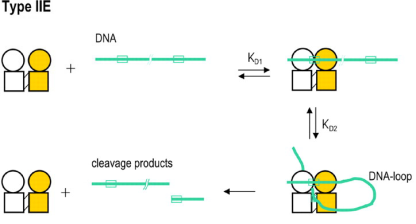
图6 Type IIE限制酶的亚基组成和切割模式
▶Type IIF
Type IIF同样是一类需要结合两个识别位点的限制酶。这类限制酶一般形成同源四聚体,四个亚基结合两个识别位点,然后同时切开两个位点上的四条 (four) DNA链(双链DNA的每个区域包含两条单链),例如SfiI (GGCCNNNN/NGGCC)。当然,有些Type IIF限制酶也属于Type IIE类,两个酶切位点中有一个可能也会产生变构效应。
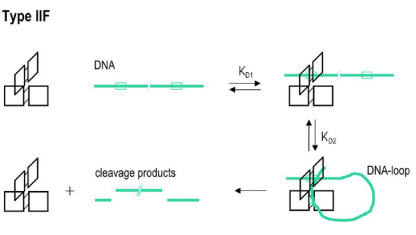
图7 Type IIF限制酶的亚基组成和切割模式
▶Type IIH
▶Type IIM
▶Type IIT

图8 Type IIT限制酶的亚基组成
05 Type III
Type III限制酶往往以同源二聚体的形式行使功能,其单体蛋白同时具有限制酶和甲基化酶两个结构域,同时还需要Mg2+、ATP和SAM作为辅助因子。Type III限制酶识别位点是同一个DNA分子上的两段反向的序列(大多数含有A),单个识别序列本身一般是非回文的,但两个识别序列反向对称。两个识别位点之间的间隔序列无特异性,长度变化较大。Type III限制酶的切割位点在其中一个识别序列之外固定距离的位置,有时切割不完全,很少被用作工具酶。
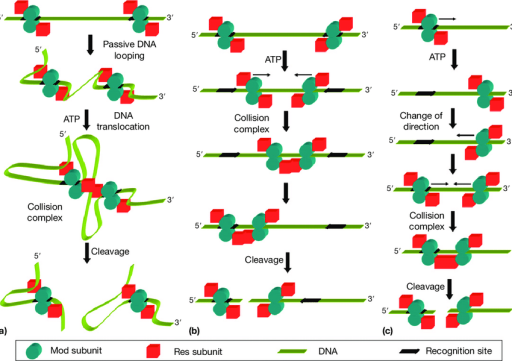
图9 Type III限制酶的几种切割模式
(a) 跟踪碰撞模型;(b) 滑动模型;(c) 一维扩散模型
但是,由于Type III限制酶的切割位点和识别位点之间的间隔(一般24~28 bp)超过Type IIS,因此一些特殊应用中也会使用Type III限制酶。例如EcoP15I (CAGCAG(25/27)) 就曾被用于基因表达系列分析 (Serial Analysis of Gene Expression,SAGE) 和亨廷顿舞蹈症的致病基因(密码子CAG出现异常重复)分析。
06 Type IV
Type IV限制酶最初是在T4噬菌体与大肠杆菌的相互作用中被发现的。这类酶组成形式多样,不同种类可以识别并切割m6A、m5C、hm5C等多种甲基化位点,但序列特异性较差。被人们熟知的是来自大肠杆菌的McrA、McrBC和Mrr。在某些工程菌株中,Type IV限制酶的编码基因需要被突变或敲除,以免影响外源基因表达。
近年来,随着表观遗传学飞速发展,研究者发现不同的Type IV限制酶可以区分不同的甲基化修饰形式,于是尝试将Type IV限制酶用作表观遗传学研究,例如使用McrBC分析CpG二核苷酸的甲基化状态。
结语
限制酶作为基因工程最早也是最基础的工具酶,仍发挥着强大的生命力。伴随着基因组学,尤其是宏基因组学的发展,仍不断有新的限制酶被测序鉴定出来,不断丰富着生物学家的武器库。
愚公生物在限制酶领域探索多年,目前产品已经覆盖了Type IIP(含Type IIE、Type IIF)、Type IIS、Type IIM、切刻内切酶等多个亚类。未来我们将继续扎根细分领域,不断推出新的限制酶产品,为中国生物医学行业提供更多优质、经济、使用方便的工具,助推中国生物医药产业发展。
参考文献:
1. Loenen et al. (2014) Nucleic Acids Res, 42(1):3-19
2. Loenen and Raleigh (2014) Nucleic Acids Res, 42(1):56-69
3. Mucke et al. (2013) Nucleic Acids Res, 31(21):6079-6084
4. Pingoud et al. (2014) Nucleic Acids Res, 42(12):7489-7527
5. Rao and Bheemanaik. (2013) Encyclopedia of Biological Chemistry, 2nd Edition. 136-141
6. Rao et al. (2014) Nucleic Acids Res, 42(1): 45-55